1
2
3
4
5
6
7
8
9
10
11
12
13
14
15
16
17
18
19
20
21
22
23
24
25
26
27
28
29
30
31
32
33
34
35
36
37
38
39
40
41
42
43
44
45
46
47
48
49
50
51
52
53
54
55
56
57
58
59
60
61
62
63
64
65
66
67
68
69
70
71
72
73
74
75
76
77
78
79
80
81
82
83
84
85
86
87
88
89
90
91
92
93
94
95
96
97
98
99
100
101
102
103
104
105
106
107
108
109
110
111
112
113
114
115
116
117
118
119
120
121
122
123
124
125
126
127
128
129
130
131
132
133
134
135
136
137
138
139
| # -*- coding: utf-8 -*-
import time
import json
import requests
from datetime import datetime
import numpy as np
import matplotlib
import matplotlib.figure
from matplotlib.font_manager import FontProperties
from matplotlib.backends.backend_agg import FigureCanvasAgg
from matplotlib.patches import Polygon
from matplotlib.collections import PatchCollection
from mpl_toolkits.basemap import Basemap
import matplotlib.pyplot as plt
import matplotlib.dates as mdates
plt.rcParams['font.sans-serif'] = ['FangSong'] # 设置默认字体
plt.rcParams['axes.unicode_minus'] = False # 解决保存图像时'-'显示为方块的问题
def catch_daily():
"""抓取每日确诊和死亡数据"""
url = 'https://view.inews.qq.com/g2/getOnsInfo?name=wuwei_ww_cn_day_counts&callback=&_=%d'%int(time.time()*1000)
data = json.loads(requests.get(url=url).json()['data'])
data.sort(key=lambda x:x['date'])
date_list = list() # 日期
confirm_list = list() # 确诊
suspect_list = list() # 疑似
dead_list = list() # 死亡
heal_list = list() # 治愈
for item in data:
month, day = item['date'].split('.')
date_list.append(datetime.strptime('2020-%s-%s'%(month, day), '%Y-%m-%d'))
confirm_list.append(int(item['confirm']))
suspect_list.append(int(item['suspect']))
dead_list.append(int(item['dead']))
heal_list.append(int(item['heal']))
return date_list, confirm_list, suspect_list, dead_list, heal_list
def catch_distribution():
"""抓取行政区域确诊分布数据"""
data = {'西藏':0}
url = 'https://view.inews.qq.com/g2/getOnsInfo?name=wuwei_ww_area_counts&callback=&_=%d'%int(time.time()*1000)
for item in json.loads(requests.get(url=url).json()['data']):
if item['area'] not in data:
data.update({item['area']:0})
data[item['area']] += int(item['confirm'])
return data
def plot_daily():
"""绘制每日确诊和死亡数据"""
date_list, confirm_list, suspect_list, dead_list, heal_list = catch_daily() # 获取数据
plt.figure('2019-nCoV 疫情统计图表', facecolor='#f4f4f4', figsize=(10, 8))
plt.title('2019-nCoV 疫情曲线', fontsize=20)
plt.plot(date_list, confirm_list, label='确诊')
plt.plot(date_list, suspect_list, label='疑似')
plt.plot(date_list, dead_list, label='死亡')
plt.plot(date_list, heal_list, label='治愈')
plt.gca().xaxis.set_major_formatter(mdates.DateFormatter('%m-%d')) # 格式化时间轴标注
plt.gcf().autofmt_xdate() # 优化标注(自动倾斜)
plt.grid(linestyle=':') # 显示网格
plt.legend(loc='best') # 显示图例
plt.rcParams['savefig.dpi'] = 300 #图片像素
plt.rcParams['figure.dpi'] = 300 #分辨率
plt.savefig('2019-nCoV 疫情曲线.png') # 保存为文件
#plt.show()
def plot_distribution():
"""绘制行政区域确诊分布数据"""
data = catch_distribution()
font = FontProperties(fname='res/SourceHanSerifCN-Regular.otf', size=14) # 自定义字体
lat_min = 0
lat_max = 60
lon_min = 70
lon_max = 140
handles = [
matplotlib.patches.Patch(color='#ffaa85', alpha=1, linewidth=0),
matplotlib.patches.Patch(color='#ff7b69', alpha=1, linewidth=0),
matplotlib.patches.Patch(color='#bf2121', alpha=1, linewidth=0),
matplotlib.patches.Patch(color='#7f1818', alpha=1, linewidth=0),
]
labels = [ '1-9人', '10-99人', '100-999人', '>1000人']
fig = matplotlib.figure.Figure()
fig.set_size_inches(10, 8) # 设置绘图板尺寸
axes = fig.add_axes((0.1, 0.12, 0.8, 0.8)) # rect = l,b,w,h
m = Basemap(llcrnrlon=lon_min, urcrnrlon=lon_max, llcrnrlat=lat_min, urcrnrlat=lat_max, resolution='l', ax=axes)
m.readshapefile('res/china-shapefiles-master/china', 'province', drawbounds=True)
m.readshapefile('res/china-shapefiles-master/china_nine_dotted_line', 'section', drawbounds=True)
m.drawcoastlines(color='black') # 洲际线
m.drawcountries(color='black') # 国界线
m.drawparallels(np.arange(lat_min,lat_max,10), labels=[1,0,0,0]) #画经度线
m.drawmeridians(np.arange(lon_min,lon_max,10), labels=[0,0,0,1]) #画纬度线
for info, shape in zip(m.province_info, m.province):
pname = info['OWNER'].strip('\x00')
fcname = info['FCNAME'].strip('\x00')
if pname != fcname: # 不绘制海岛
continue
for key in data.keys():
if key in pname:
if data[key] == 0:
color = '#f0f0f0'
elif data[key] < 10:
color = '#ffaa85'
elif data[key] <100:
color = '#ff7b69'
elif data[key] < 1000:
color = '#bf2121'
else:
color = '#7f1818'
break
poly = Polygon(shape, facecolor=color, edgecolor=color)
axes.add_patch(poly)
axes.legend(handles, labels, bbox_to_anchor=(0.5, -0.11), loc='lower center', ncol=4, prop=font)
axes.set_title("2019-nCoV 疫情地图", fontproperties=font)
FigureCanvasAgg(fig)
plt.rcParams['savefig.dpi'] = 300 #图片像素
plt.rcParams['figure.dpi'] = 300 #分辨率
fig.savefig('2019-nCoV 疫情地图.png')
if __name__ == '__main__':
plot_daily()
plot_distribution()
|
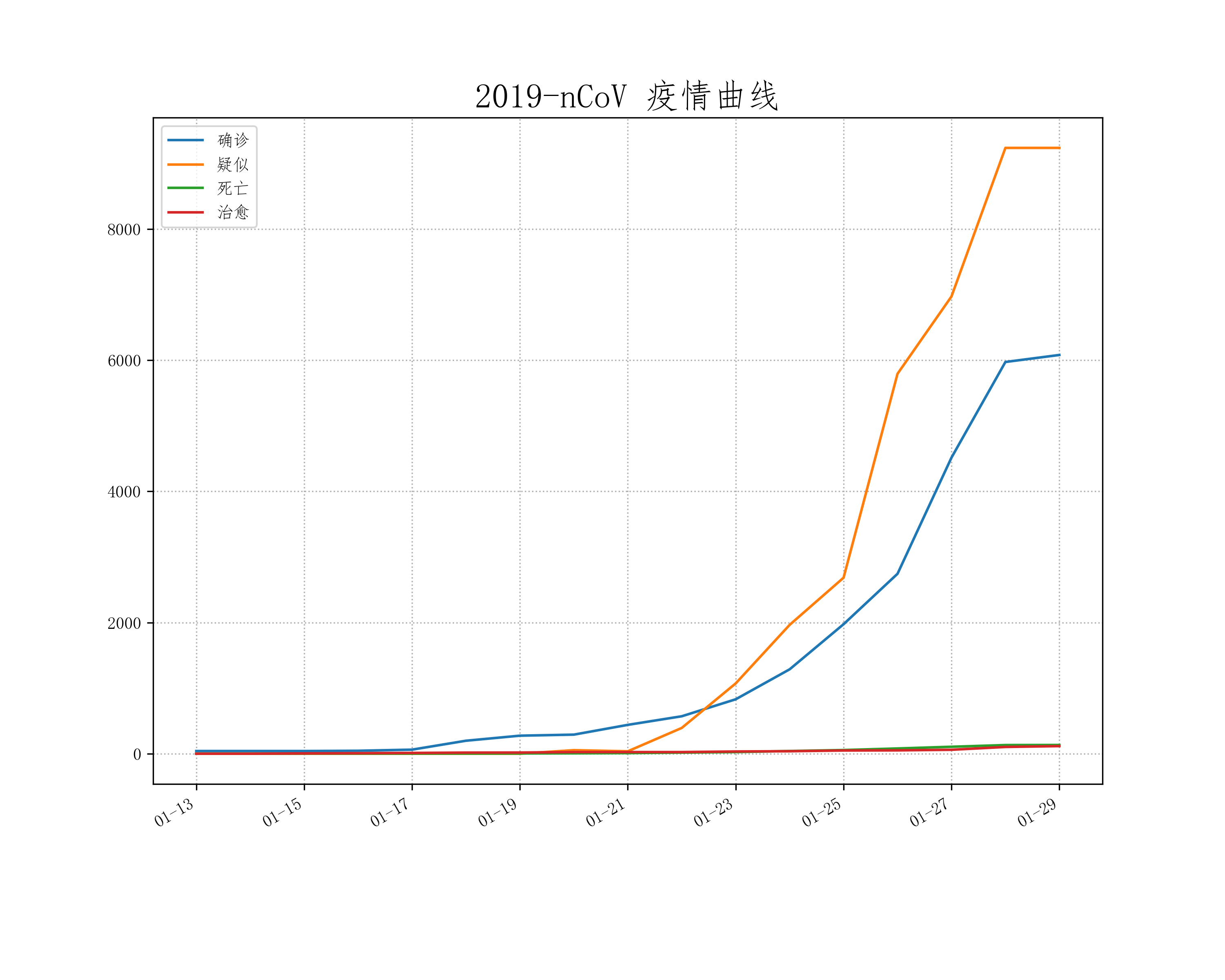 ※ 疫情曲线
※ 疫情曲线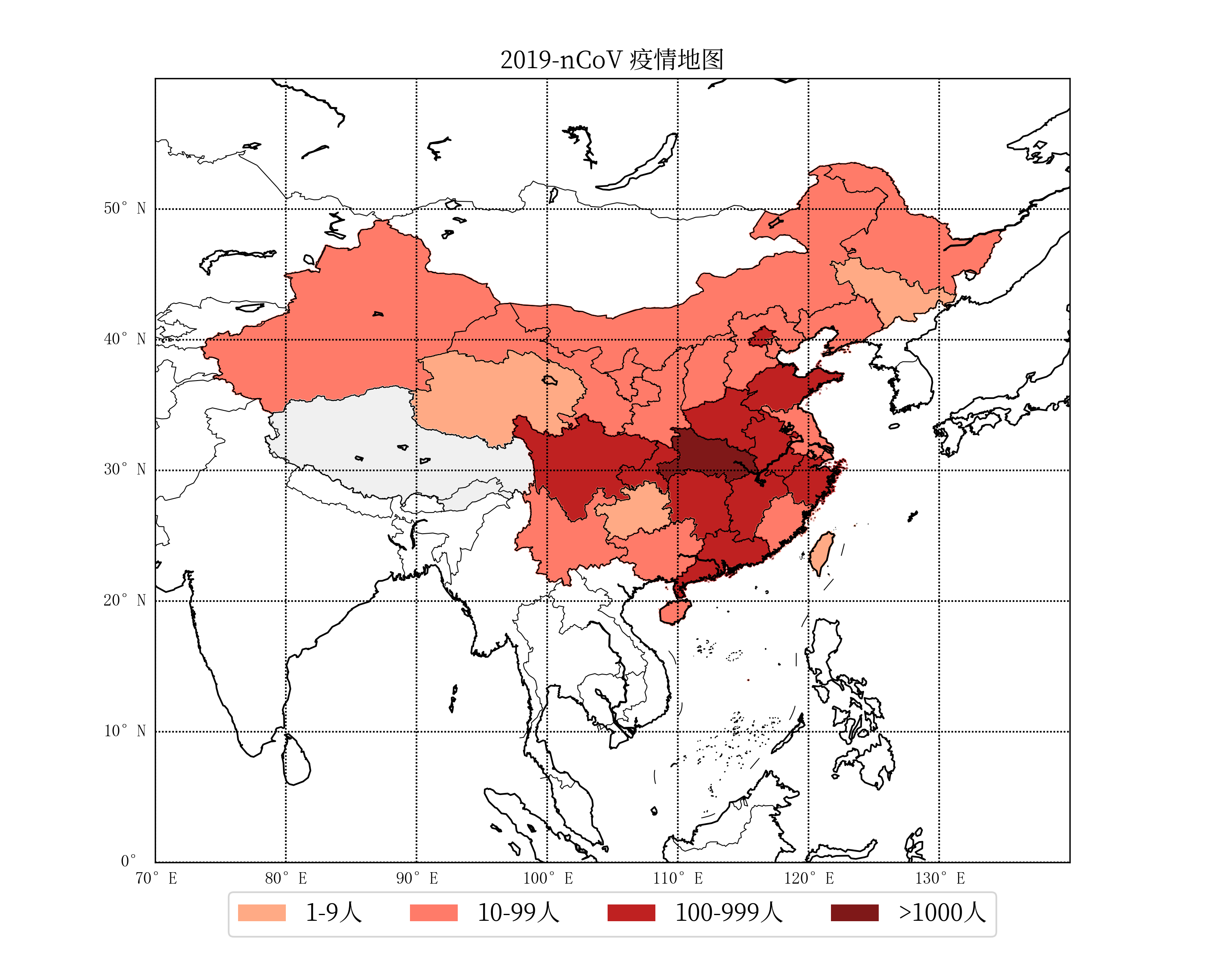 ※ 圆柱投影疫情地图
※ 圆柱投影疫情地图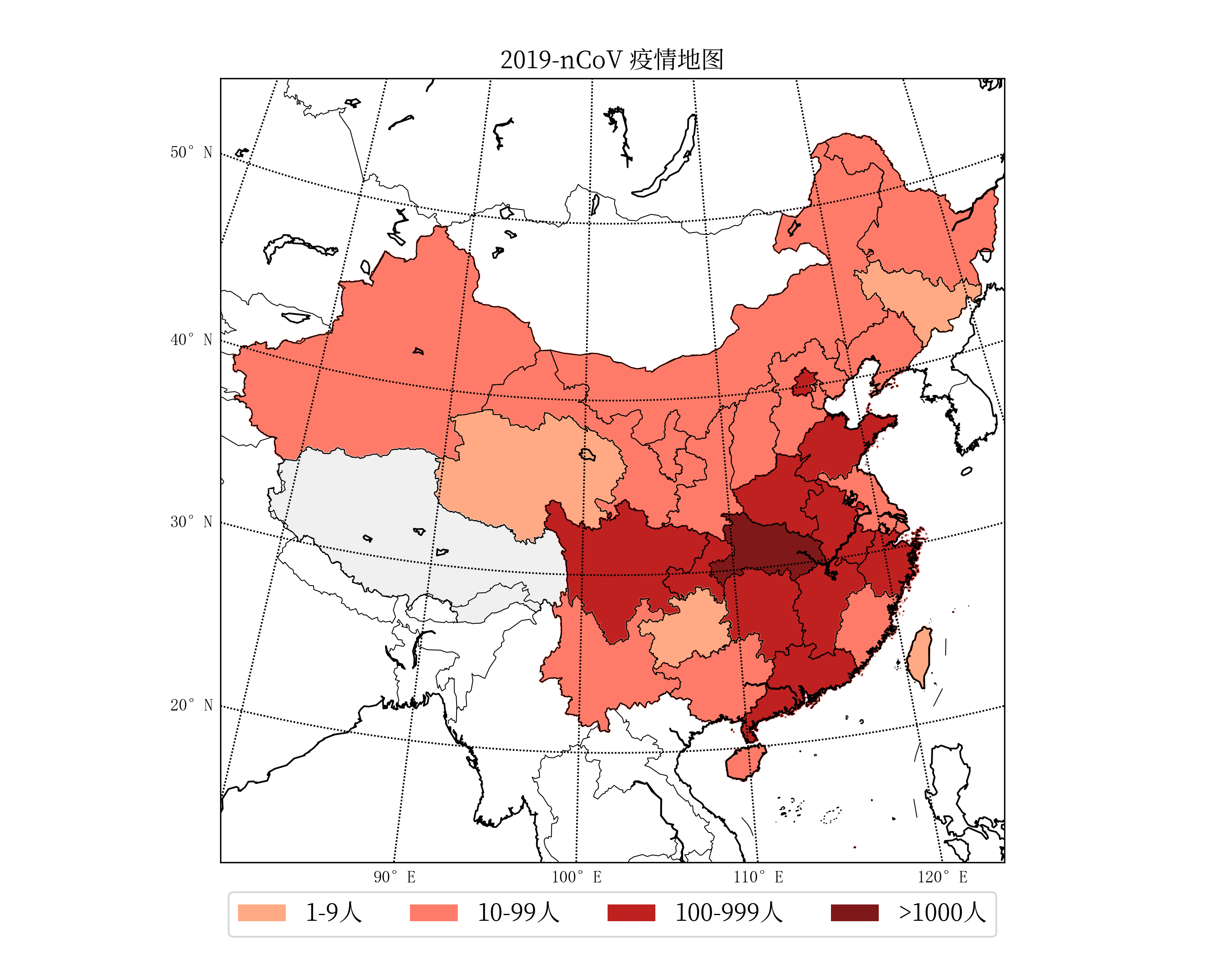 ※ 兰勃特投影疫情地图
※ 兰勃特投影疫情地图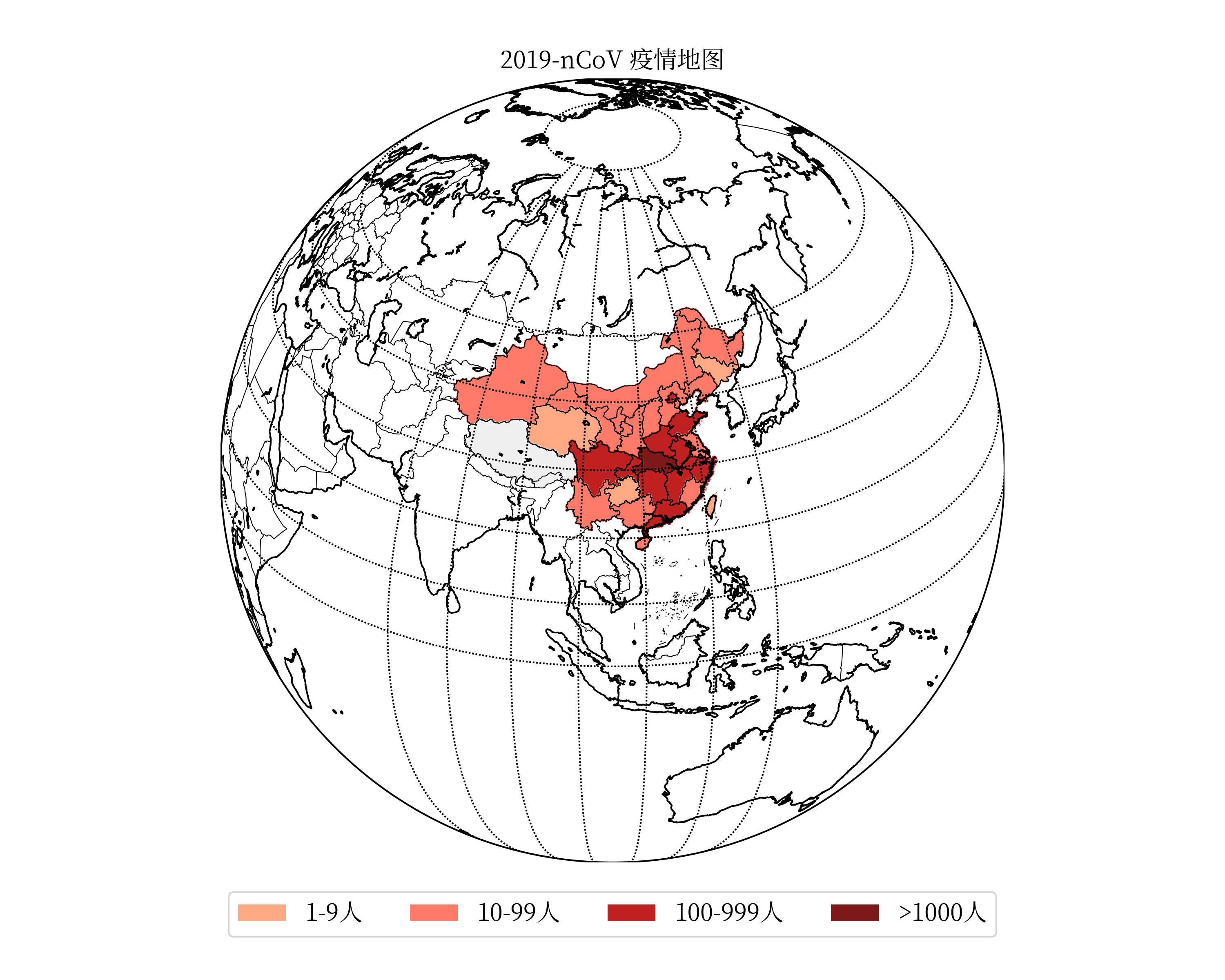 ※ 正射投影疫情地图
※ 正射投影疫情地图